- Prodotti
- Modulo software di analisi
- JSI medical systems
Modulo software per sequenziamento SEQPATIENTdi analisida laboratorio
Aggiungi ai preferiti
Confronta con altri prodotti
Vuoi acquistare direttamente?
Vai sul nostro Shop.
Caratteristiche
- Funzione
- di analisi
- Applicazioni
- per sequenziamento, da laboratorio
Descrizione
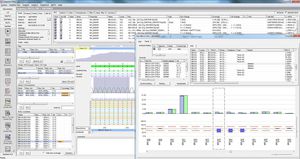
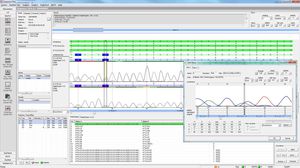
SEQPATIENT è un'applicazione potente e di facile utilizzo per l'allineamento e il rilevamento di varianti di dati di sequenziamento Sanger. SEQPATIENT è in grado di analizzare i dati di tutte le più comuni piattaforme di sequenziamento. La visualizzazione di tutte le varianti rilevate, come delezioni, inserzioni, indel e SNP, è chiara e intuitiva. È possibile analizzare il DNA genomico e il cDNA. Una funzione statistica dell'area di picco garantisce il rilevamento di mutazioni a bassa frequenza, come abbandoni allelici, mosaici e varianti somatiche.
SEQPATIENT offre l'accesso a database pubblici di SNP come dbSNP, 1000 Genomes, COSMIC, ClinVar, ClinVitae, ExAC e gnomAD per la classificazione e il filtraggio. Tutti i dati dei risultati possono essere scambiati con il nostro database delle varianti per la Shared Experience And Knowledge - varSEAK, trasferiti ai sistemi LIM interni del laboratorio e/o rilasciati come referti personalizzati per i pazienti.
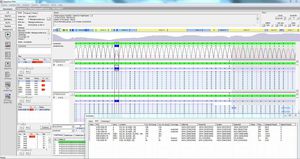
Compatibile con i dati di tutte le più comuni piattaforme di sequenziamento Sanger
Facile impostazione di singole regioni target tramite l'importazione di file txt o bed basati su singoli geni scaricati (ENSEMBL / NCBI) o hg19 / hg38
Chiamatore di basi configurabile con soglie dipendenti dal sequenziatore
Taglio automatico e definito dall'utente dei file dei risultati del sequenziamento
Identificazione del paziente e genotipizzazione tramite ID SNP
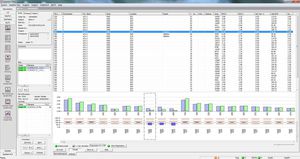
Tutti i risultati di un paziente sono visualizzati in un'unica schermata, comprese le varianti trovate, le modifiche aminoacidiche, le nomenclature HGVS ecc.
Elevata sensibilità e specificità per il rilevamento di SNP, delezioni, inserzioni e indelezioni
Database interno delle mutazioni che tiene traccia della storia del rilevamento delle mutazioni da parte di SEQPATIENT e SEQNEXT
---
Cataloghi
SEQUENCE PILOT
2 Pagine
* I prezzi non includono tasse, spese di consegna, dazi doganali, né eventuali costi d'installazione o di attivazione. I prezzi vengono proposti a titolo indicativo e possono subire modifiche in base al Paese, al prezzo stesso delle materie prime e al tasso di cambio.