- Laboratorio
- Biologia molecolare
- Software per reportistica
- JSI medical systems
Software per reportistica virSEAKd’importazioneNGSper biologia molecolare
Aggiungi ai preferiti
Confronta con altri prodotti
Vuoi acquistare direttamente?
Vai sul nostro Shop.
Caratteristiche
- Funzione
- per reportistica, d’importazione, NGS
- Applicazioni
- per biologia molecolare
- Tipo
- automatizzato
Descrizione
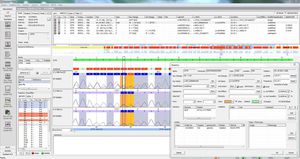
virSEAK (RUO - research use only) offre un confronto rapido e conveniente della propria sequenza di SARS-CoV-2 con le sequenze disponibili. Dopo un'impostazione personalizzata con il kit, è sufficiente caricare i dati fastq o fasta per ottenere una sequenza allineata con le varianti.
Inoltre, la vostra sequenza sarà assegnata a un lignaggio pangolino (ad esempio B.1.1.7) e a un clade GISAID (ad esempio L).
virSEAK controlla anche automaticamente se la sequenza contiene le varianti N501Y e E484K della proteina spike.
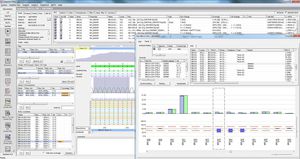
Vengono mostrati i valori di copertura e qualità, tra cui: copertura richiesta, assoluta, media e mediana, % di basi "wild type" e "N". Un indicatore di qualità mostra se la qualità soddisfa le soglie di qualità definite.
Inoltre, lo strumento è ottimizzato per il sequenziamento NGS ad alta produttività con funzioni di importazione ed esportazione automatizzate e trasferimento personalizzabile della sequenza. È possibile creare facilmente file multi-fasta per migliorare la segnalazione a un ufficio centrale per la sorveglianza della situazione epidemiologica e della diffusione delle mutazioni (ad esempio, in Germania il Robert Koch Institut).
virSEAK - versione installabile:
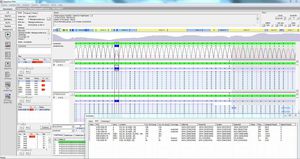
importazione semplice di file di sequenziamento fastq grezzi o fasta preprocessati
sequenziamento NGS ad alto rendimento con importazione ed esportazione automatizzata in batch
avviso automatico se sono presenti le mutazioni N501Y e/o E484K
assegnazione a un lignaggio di Pangolin e a un clade GISAID
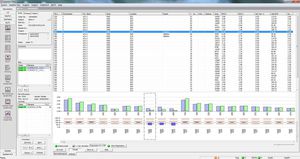
verificare la presenza di altre varianti con frequenze
confrontare i sottotipi, i conteggi e le posizioni dei reperti, ...
esportare la sequenza e le varianti (con le meta-informazioni, in formato fasta e/o csv)
i risultati vengono archiviati
sequenziamento high-throughput completamente automatizzato con trasferimento della sequenza personalizzabile
---
Cataloghi
Nessun catalogo è disponibile per questo prodotto.
Vedi tutti i cataloghi di JSI medical systemsRicerche correlate
- Software medicale di analisi
- Software per reportistica
- Software automatizzato
- Modulo software
- Software d’importazione
- Software server
- Modulo software di analisi
- Software per biologia molecolare
- Modulo software da laboratorio
- Modulo software di acquisizione
- Modulo software di controllo
- Software NGS
- Modulo software di cartografia
* I prezzi non includono tasse, spese di consegna, dazi doganali, né eventuali costi d'installazione o di attivazione. I prezzi vengono proposti a titolo indicativo e possono subire modifiche in base al Paese, al prezzo stesso delle materie prime e al tasso di cambio.